cluster
リンケージによる凝集型クラスターの構築
説明
T = cluster(Z,Cutoff=cutoff)Z からクラスターを定義します。入力 Z は、入力データ行列 X に対する linkage 関数の出力です。cluster は、ツリー内のノードの不整合係数 (または inconsistent の値) のしきい値として cutoff を使用して、Z をクラスターに分割します。出力 T には、各観測値 (X の行) のクラスター割り当てが格納されます。
T = cluster(___,Name=Value)cluster(Z,MaxClust=5,Depth=3) と指定します。
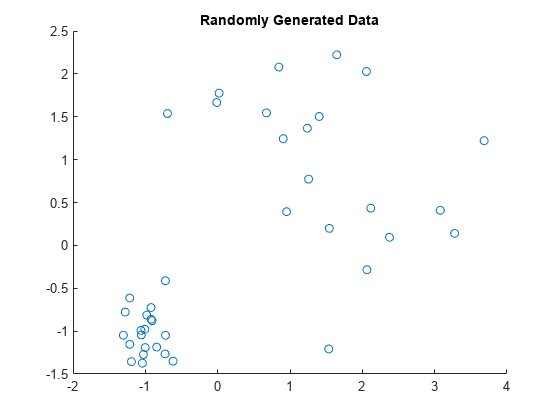
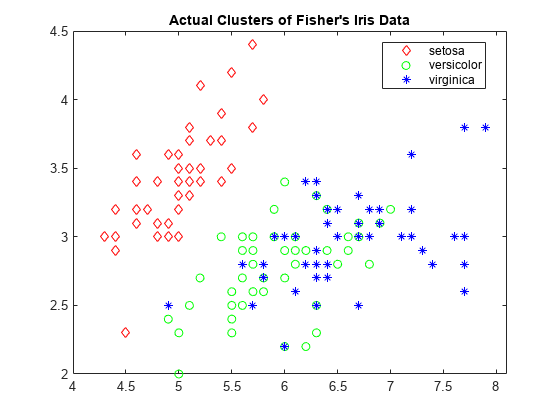
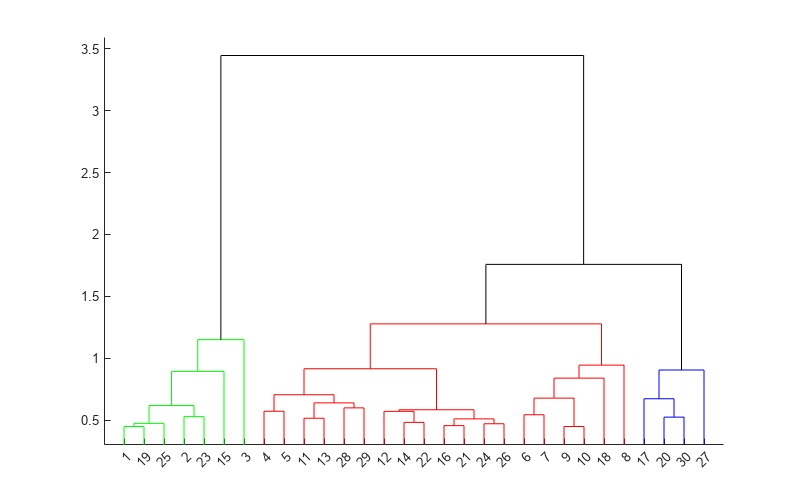
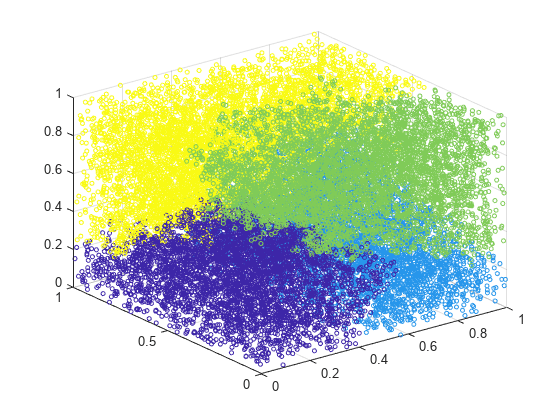
例
入力引数
名前と値の引数
出力引数
代替機能
入力データ行列 X がある場合、clusterdata を使用すると、凝集型クラスタリングを実行して、X 内の各観測値 (行) のクラスター インデックスを取得できます。関数 clusterdata は必要な手順をすべて実行するので、関数 pdist、linkage および cluster を個別に実行する必要はありません。